Diversidad genética humana: variación genómica
Variación genómica
La gran mayoría de las letras del ADN en los genomas de las personas son idénticas, pero una pequeña fracción de esas letras varía. La diversidad genética humana se origina a partir de variaciones que pueden ocurrir desde el nivel de nucleótidos individuales hasta segmentos completos de cromosomas. La variación genómica puede desempeñar un papel en las enfermedades, en la susceptibilidad a enfermedades o ser completamente benigna.

¿Qué es el genoma humano?
Un genoma es el conjunto completo de instrucciones de ADN que se encuentra en cada célula. El ADN está compuesto por cuatro sustancias químicas diferentes (llamadas nucleótidos o bases), representadas por letras: adenina (A), timina (T), citosina (C) y guanina (G). El orden de estas letras —es decir, la secuencia del ADN— codifica la información que le dice a cada célula qué hacer y cuándo hacerlo. El ADN del genoma está organizado en estructuras llamadas cromosomas.
Una copia del genoma humano contiene aproximadamente 3 mil millones de nucleótidos, distribuidos entre 23 cromosomas. La mayoría de las células humanas poseen dos copias del genoma, una heredada de cada progenitor. Las células con dos copias de cada cromosoma se conocen como diploides. La mayoría de los mamíferos, incluyendo a los humanos, son diploides, aunque existen organismos que tienen un solo conjunto o más de dos conjuntos de cromosomas.
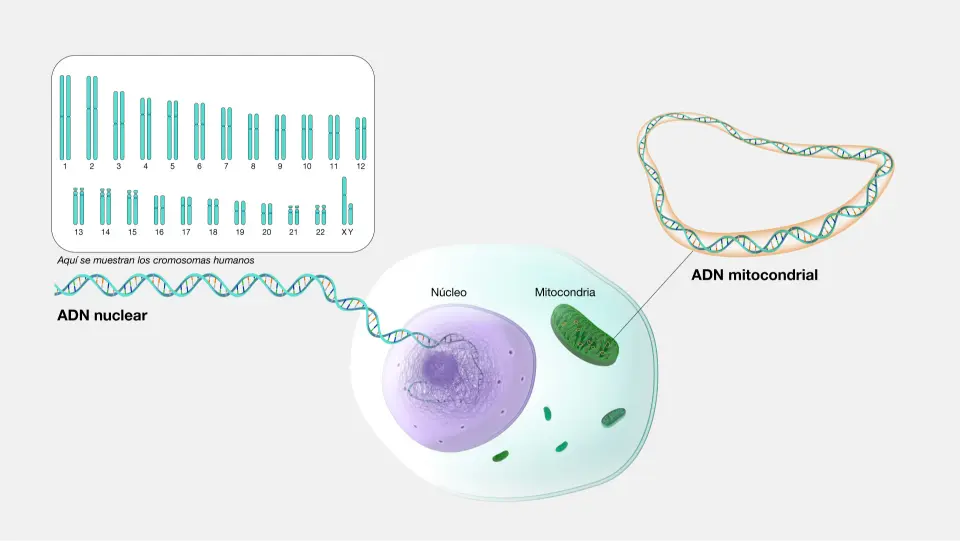
Un segmento de ADN que ocupa una posición o ubicación particular en un cromosoma se llama locus (plural loci). Un locus puede ser grande, quizás conteniendo muchos genes, puede ser un solo gen o puede ser sólo una base individual en el genoma.
Las versiones alternativas de la secuencia de ADN en un locus se llaman alelos. Para muchos genes, existe un alelo predominante, usualmente presente en más de la mitad de los individuos en una población, que los genetistas llaman alelo tipo silvestre o alelo común. Las otras versiones del gen son alelos variantes que difieren del alelo tipo silvestre debido al efecto de una mutación que ha cambiado la secuencia o el arreglo de nucleótidos en el ADN.
¿Cómo varían los genomas entre las personas?
Los genomas humanos son mucho más parecidos entre sí de lo que son diferentes. Frecuentemente se afirma que los genomas de dos personas cualesquiera son aproximadamente un 99.9 % idénticos. Este porcentaje se basa en el hallazgo de que, en promedio, existe una diferencia de un solo nucleótido cada 1,300 nucleótidos entre los genomas de dos personas.
Sin embargo, esta cifra es una simplificación, ya que solo toma en cuenta las diferencias de un solo nucleótido. En realidad, cualquier par de genomas humanos es, en promedio, ~99.6 % idéntico y ~0.4 % diferente. Este 0.4 % incluye tanto las diferencias de nucleótido único como las que involucran múltiples nucleótidos.

Estas diferencias entre los genomas humanos se conocen como variantes genómicas. El conjunto de variantes genómicas de una persona forma parte de lo que la hace única. Otros factores —como la alimentación, el entorno, el estilo de vida y el contexto social— también contribuyen a esa individualidad.
La mayoría de las variantes genómicas no tienen ningún efecto sobre el funcionamiento del genoma. Sin embargo, un pequeño subconjunto de ellas sí puede tener un impacto. Por ejemplo, algunas variantes influyen en características físicas como el color de ojos o la estatura; otras afectan la salud o la manera en que una persona responde a ciertos medicamentos.
¿Cuáles son los diferentes tipos de variantes genómicas?
Variantes de un solo nucleótido
Las variantes más pequeñas son las llamadas variantes de un solo nucleótido (single-nucleotide variants, SNVs, por sus siglas en inglés). Cada SNV representa una diferencia en un solo nucleótido (o “letra”) del ADN. Por ejemplo, en una determinada posición del genoma, una persona puede tener una C, mientras que otra puede tener una T. Las SNVs son el tipo más común de variación genómica.
Un subtipo de SNVs se conoce como polimorfismo de un solo nucleótido (single-nucleotide polymorphism, SNP, pronunciado “snip”). Para que una SNV sea considerada un SNP, debe estar presente en al menos el 1 % de la población humana. Por lo tanto, el término SNV es más general e incluye tanto las diferencias comunes (como los SNPs) como las raras.

Un locus polimórfico caracterizado por una SNV común generalmente tiene solo dos alelos, que corresponden a dos bases diferentes en esa ubicación particular. Las SNVs comunes se observan, en promedio, una vez cada 1000 pares de bases. Sin embargo, su distribución es desigual en todo el genoma; muchas más se encuentran en regiones no codificantes del genoma, en intrones y en secuencias que están a cierta distancia de los genes codificantes de proteínas.
No obstante, una cantidad significativa de SNVs, tanto comunes como raras, ocurren en genes y otros elementos funcionales conocidos del genoma. Aproximadamente la mitad de estas no alteran la secuencia de aminoácidos predicha de la proteína codificada y, por lo tanto, se denominan sinónimas, mientras que aquellas que sí alteran la secuencia de aminoácidos se llaman no sinónimas. Otras SNVs son candidatas a tener consecuencias funcionales significativas, ya que introducen o modifican un codón de paro o alteran un sitio de empalme (splicing) conocido.
El significado para la salud de la gran mayoría de las SNVs comunes es desconocido y constituye el objeto de investigaciones en curso. El hecho de que estas variantes sean comunes no significa que estén exentas de efectos perjudiciales o protectores sobre la salud o la longevidad. Lo que sí significa es que cualquier efecto de las SNVs comunes probablemente implique una alteración relativamente sutil de la susceptibilidad a enfermedades, más que ser una causa directa de una enfermedad grave.
Inserciones y deleciones
Otro grupo de variantes genómicas pequeñas son las inserciones y deleciones (conocidas como indels). Estas variantes reflejan nucleótidos adicionales (inserciones) o faltantes (deleciones) en el genoma, y por lo general implican menos de 50 nucleótidos. Aunque las indels son menos frecuentes que las SNVs, pueden tener un impacto mayor en la salud y la enfermedad, por ejemplo, si interrumpen el funcionamiento de un gen que codifica una proteína importante.
Aproximadamente la mitad de todos los indeles se denominan simples porque tienen solo dos alelos, es decir, la presencia o ausencia del segmento insertado o eliminado.
Variantes de Microsatélites
Uno de los tipos más comunes de indels son los repetidos en tándem (también llamados microsatélites). Se trata de tramos cortos de nucleótidos que se repiten varias veces de forma consecutiva y que son altamente variables entre personas.
Estas variantes son multialélicas debido al número variable de un segmento de ADN repetido en tándem en una ubicación particular y pueden repetirse desde unas pocas veces hasta cientos de veces, dependiendo del cromosoma y del individuo. A veces llamados repeticiones en tándem de número variable (VNTR, por sus siglas en inglés), estos microsatélites son altamente susceptibles a mutaciones.

Consisten en segmentos de ADN compuestos por unidades de varios nucleótidos —como TG, CAA o AAAT— repetidos en tándem entre una y unas pocas docenas de veces. El número de unidades repetidas determina los diferentes alelos, que a veces también se denominan repeticiones cortas en tándem (STR, por sus siglas en inglés). Un locus de microsatélite suele tener muchos alelos (longitudes de repetición) que pueden evaluarse rápidamente mediante procedimientos de laboratorio estándar para distinguir entre diferentes individuos e inferir relaciones familiares. Se conocen decenas de miles de loci de microsatélites distribuidos por todo el genoma humano.
Determinar los alelos en múltiples loci de microsatélites es actualmente el método preferido para la huella genética utilizada en pruebas de identidad. Por ejemplo, el FBI de los EE. UU. utiliza actualmente 20 STR en su panel de identificación genética. Es tan poco probable que dos individuos (excepto gemelos monocigóticos) tengan exactamente los mismos alelos en los 20 loci que este panel permite una determinación prácticamente definitiva de si dos muestras provienen del mismo individuo.
Variantes por Inserción de Elementos Móviles
Aunque la mayoría de las copias de estos elementos repetidos son estacionarias, algunas son móviles y contribuyen a la diversidad genética humana mediante el proceso de retrotransposición; este proceso implica la transcripción a ARN, la retrotranscripción a una secuencia de ADN y la inserción (es decir, transposición) en otro sitio del genoma.
Las dos familias de elementos móviles más comunes son las familias de repeticiones Alu y LINE (elementos nucleares intercalados largos), y se han descrito cerca de 10,000 variantes por inserción de elementos móviles en diferentes poblaciones. Cada locus polimórfico consta de dos alelos: uno con el elemento móvil insertado y otro sin él.
Las variantes de elementos móviles se encuentran en todos los cromosomas humanos; aunque la mayoría se localizan en regiones no génicas, una pequeña proporción se encuentra dentro de genes. En muchos de estos loci, el alelo con inserción tiene una frecuencia superior al 10% en diversas poblaciones.
Variantes estructurales
La variación genómica no se limita a tramos pequeños, sino que también puede abarcar regiones cromosómicas más grandes. Estas diferencias de gran escala se conocen como variantes estructurales y afectan al menos 50 nucleótidos, aunque pueden involucrar miles. Estas variantes pueden incluir inserciones, deleciones, inversiones o reubicaciones de segmentos del genoma.

Cuando una variante estructural implica una diferencia en el número total de nucleótidos, se denomina variante en el número de copias (copy-number variant, CNV), que están conceptualmente relacionadas con los indels y los microsatélites, pero que involucran segmentos más grandes del genoma, definidos como aquellos que van desde 1000 pares de bases hasta aproximadamente 3 millones de pares de bases
Las CNVs se distinguen de otras variantes estructurales como las inversiones y translocaciones, ya que estas últimas no suelen implicar cambios en la cantidad total de material genético.

En la población general, se encuentran variantes mayores de 500 kb en el 5% al 10% de los individuos, y aquellas que abarcan más de 1 Mb en el 1% al 2%.
Como ocurre con los indel, los CNVs más pequeños pueden tener solo dos alelos (es decir, la presencia o ausencia de un segmento). Algunos CNVs grandes tienen múltiples alelos debido a la presencia de diferentes números de copias en tándem de un segmento de ADN.
¿Cuál es el inventario de variantes genómicas en una secuencia típica del genoma humano?
En promedio, comparado con un genoma humano de referencia, la secuencia genómica de una persona de aproximadamente 6 mil millones de nucleótidos tendrá:
- ~5,000,000 de SNVs que involucran aproximadamente 5,000,000 de nucleótidos
- ~600,000 variantes de inserción/deleción que involucran aproximadamente 2,000,000 de nucleótidos
- ~25,000 variantes estructurales que involucran más de 20,000,000 de nucleótidos.

Esto significa que, en promedio, el conjunto completo de variantes genómicas en el genoma de cada persona involucra alrededor de 27,000,000 de nucleótidos (de los aproximadamente 6,000,000,000 de nucleótidos en su genoma). Esos ~27,000,000 de nucleótidos reflejan algún tipo de diferencia en esas posiciones del ADN, representando aproximadamente el 0.4% del genoma completo de la persona.
En otras palabras, al considerar el inventario completo de variantes genómicas, la secuencia del genoma típico de una persona es aproximadamente 99.6% idéntica (o un 0.4% diferente) a una secuencia de genoma humano de referencia (o incluso al genoma de otra persona).
¿Por qué importa la variación genómica?
La variación genómica impulsa la evolución y contribuye a expandir la biodiversidad. Esto es cierto tanto para los humanos como para las plantas, animales y otros organismos. Esta diversidad mantiene saludables a las poblaciones y es fundamental para la selección natural, un proceso evolutivo mediante el cual los organismos se adaptan a entornos cambiantes.
La variación genómica humana también es muy relevante en el campo de la medicina. Solo una pequeña fracción de las variantes genómicas afecta la salud humana. En algunos casos, las variantes genómicas causan enfermedades directamente (como en la fibrosis quística y la anemia de células falciformes). En otros casos, los efectos de las variantes genómicas son más sutiles (como en la hipertensión y la diabetes, donde una variante genómica puede contribuir al riesgo general que una persona tiene de desarrollar la condición).

Los profesionales de la salud están aprendiendo cada vez más a utilizar la información sobre las variantes genómicas de los pacientes para manejar su atención médica, algo conocido como medicina genómica.
Conclusión
La variación genómica es una característica inherente a la especie humana y constituye una fuente fundamental de diversidad biológica. Aunque los genomas humanos son en su mayoría idénticos, el pequeño porcentaje de diferencias —ya sea en un solo nucleótido o en segmentos completos del ADN— tiene un profundo impacto en nuestra individualidad, evolución y salud. Comprender los distintos tipos de variantes genómicas, desde SNVs y microsatélites hasta variantes estructurales complejas, nos permite no solo rastrear relaciones familiares o poblacionales, sino también avanzar hacia una medicina más personalizada y precisa. A medida que la tecnología de secuenciación continúa desarrollándose, nuestro conocimiento sobre la diversidad genómica humana seguirá creciendo, abriendo nuevas oportunidades para la investigación biomédica, la prevención de enfermedades y la mejora de la atención médica a nivel individual y poblacional.